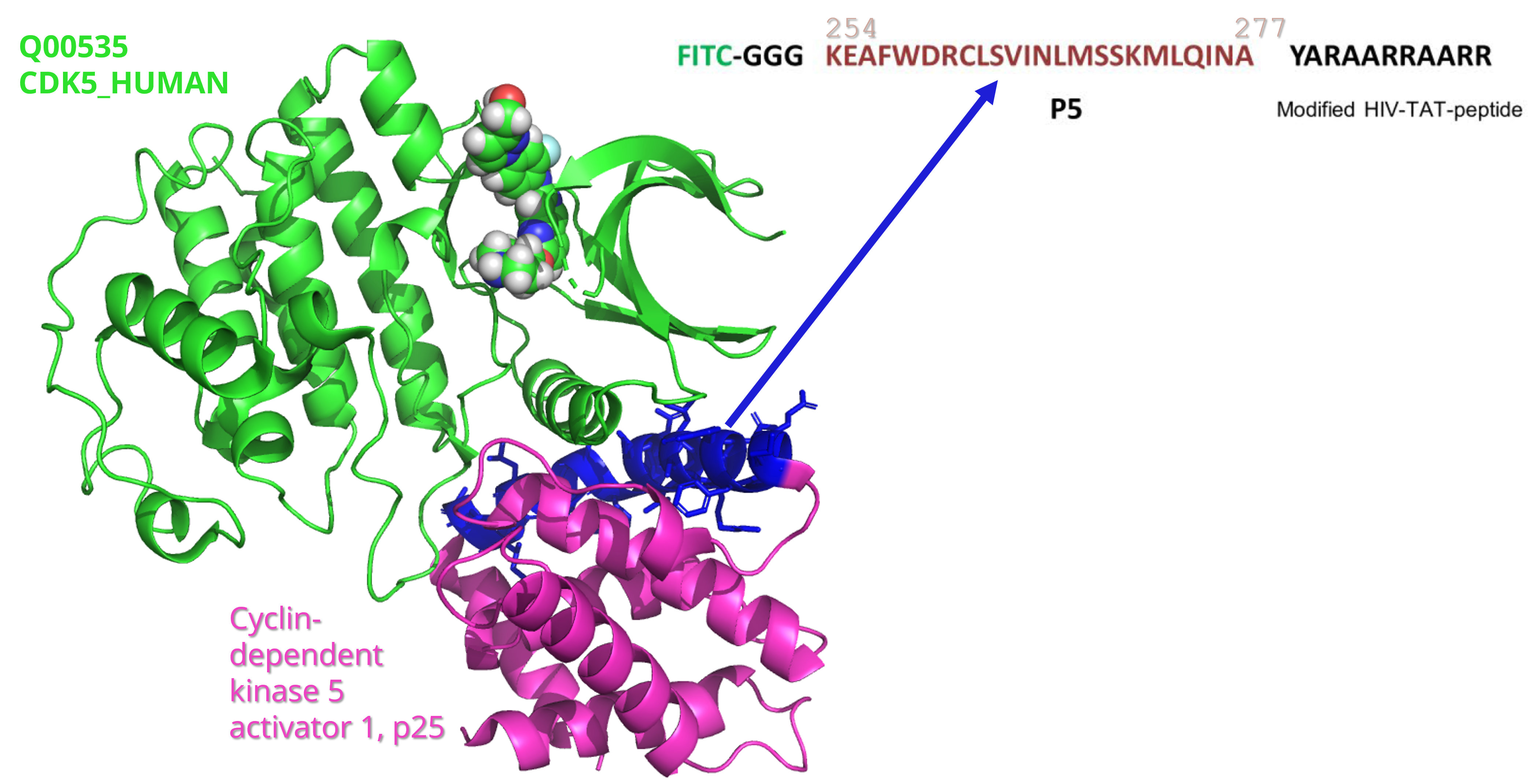
Localizar una secuencia de aminoácidos en una estructura (PyMol).
El siguiente script de Python se ejecuta desde PyMol y busca en la cadena "C" del objeto "7VDP" la secuencia de aminoácidos "KEAFWDRCLSVINLMSSKMLQINA" y si la encuentra cree un nuevo objeto llamado "peptido-P5". Logicamente se puede cambiar la cadena, el objeto, la secuencia y el nombre del objeto nuevo con el peptido que encuentre. Se permite hasta 6 errores en la secuencia (mismatches_max=6).
from pymol import cmd
# Diccionario 3→1
aa_3to1 = {
"ALA":"A","ARG":"R","ASN":"N","ASP":"D","CYS":"C",
"GLN":"Q","GLU":"E","GLY":"G","HIS":"H","ILE":"I",
"LEU":"L","LYS":"K","MET":"M","PHE":"F","PRO":"P",
"SER":"S","THR":"T","TRP":"W","TYR":"Y","VAL":"V"
}
def hamming(seq1, seq2):
return sum(a != b for a, b in zip(seq1, seq2))
def crear_peptido_desde_secuencia(objeto="7VDP", cadena="C",
secuencia_objetivo="KEAFWDRCLSVINLMSSKMLQINA",
mismatches_max=6,
nombre_objeto="peptido-P5"):
modelo = cmd.get_model(f"{objeto} and chain {cadena} and name CA")
residuos = []
secuencia_real = ""
for atom in modelo.atom:
resi = atom.resi
resn = atom.resn
if len(residuos) == 0 or residuos[-1][0] != resi:
residuos.append((resi, resn))
secuencia_real += aa_3to1.get(resn, "X")
L = len(secuencia_objetivo)
mejor_match = None
mejor_score = L + 1 # peor caso
# Sliding window
for i in range(len(secuencia_real) - L + 1):
ventana = secuencia_real[i:i+L]
dist = hamming(ventana, secuencia_objetivo)
if dist < mejor_score:
mejor_score = dist
mejor_match = i
if mejor_match is None or mejor_score > mismatches_max:
print("No se encontró ninguna región dentro del umbral de mismatches.")
print(f"Mejor coincidencia tenía {mejor_score} mismatches.")
return
print(f"Mejor match en posición: {mejor_match}")
print(f"Mismatches: {mejor_score} / {L}")
inicio = mejor_match
fin = mejor_match + L
resis_seleccionados = [residuos[i][0] for i in range(inicio, fin)]
seleccion = f"{objeto} and chain {cadena} and resi " + "+".join(resis_seleccionados)
cmd.create(nombre_objeto, seleccion)
# Información extra útil
seq_encontrada = secuencia_real[inicio:fin]
print("Secuencia encontrada:")
print(seq_encontrada)
print("Secuencia objetivo:")
print(secuencia_objetivo)
# Ejecutar
crear_peptido_desde_secuencia()